Verwendung der Bibliothek
Im folgenden Abschnitt wird die Verwendung der Bibliothek am Beispiel eines Datensatzes zur Klassifikation der Bananen-Qualität schrittweise vorgestellt. Zunächst wird der gesamte Code gezeigt, um einen Überblick zu geben. Anschließend werden die einzelnen Schritte und weitere Funktionen der KNN-Bibliothek detailliert erläutert.
Zur Verwendung muss die Bibliothek zunächst als Dependency in ein neues Projekt (z.B. mit Maven) eingebunden werden. Die Bibliothek wurde mit/für Java 21 entwickelt und sollte deshalb mit Java 21 verwendet werden.
KNN-Bibliothek (knn.jar) ins lokale Maven-Repository installieren:
# Ausführung im Verzeichnis unseres KNN-Projekts, in welchem sich die knn.jar und die pom.xml befinden
mvn install:install-file -Dfile=knn.jar -DpomFile=pom.xml
# Alternativ kann auch der Quellcode des KNN-Projekts direkt gebaut und installiert werden
mvn clean installMaven-Dependency der pom.xml des neuen Projekts hinzufügen:
<dependencies>
<dependency>
<groupId>de.fhdw</groupId>
<artifactId>knn</artifactId>
<version>1.0.0</version>
</dependency>
</dependencies>Alternativ kann die knn.jar auch manuell in das Projekt eingebunden werden (z.B. über IntelliJ, Eclipse, etc.)
Beispiel-Code
Vollständige/ausführbare Klasse für dieses Beispiel siehe de.fhdw.knn.run.BananaQuality
package de.fhdw.knn.run;
import de.fhdw.knn.scorer.ClassificationScorer;
import de.fhdw.knn.data.CsvReader;
import de.fhdw.knn.data.DataSet;
import de.fhdw.knn.data.TrainTestSplit;
import de.fhdw.knn.network.Network;
import de.fhdw.knn.network.activation.ActivationFunction;
import de.fhdw.knn.network.connection.WeightInitializer;
import de.fhdw.knn.network.layer.DenseLayer;
import de.fhdw.knn.scorer.Score;
import de.fhdw.knn.scorer.Scorer;
import de.fhdw.knn.trainer.Trainer;
import de.fhdw.knn.trainer.learningrate.ConstantLearningRate;
import de.fhdw.knn.trainer.learningrate.LearningRateFunction;
import de.fhdw.knn.trainer.loss.LossFunction;
import de.fhdw.knn.trainer.optimization.GradientDescent;
import de.fhdw.knn.trainer.optimization.OptimizationFunction;
import de.fhdw.knn.trainer.stop.EarlyStopping;
import de.fhdw.knn.trainer.stop.StopFunction;
import de.fhdw.knn.visualization.HeatmapData;
import de.fhdw.knn.visualization.HeatmapView;
import de.fhdw.knn.visualization.SankeyData;
import de.fhdw.knn.visualization.SankeyView;
import javafx.application.Platform;
import java.io.IOException;
public class BananaQuality {
public static void main(String[] args) throws IOException {
/// Datenaufbereitung
DataSet data = CsvReader.readFile("data/banana_quality.csv", 0, 7, 7, 1);
/// optional Inputs (oder Outputs) normalisieren
// Normalizer inputNormalizer = new MinMaxNormalizer(-10, 10);
// data.normalizeInputs(inputNormalizer);
/// Train-/Test-Split erzeugen
TrainTestSplit trainTest = data.shuffleAndSplit(42, 0.2);
DataSet train = trainTest.train;
DataSet test = trainTest.test;
/// Netzwerk erzeugen
DenseLayer[] denseLayers = DenseLayer.createLayers(
ActivationFunction.SWISH, ActivationFunction.SIGMOID,
100, 100, 1);
Network network = new Network(42, WeightInitializer.GLOROT_UNIFORM,
7, denseLayers);
/// alternativ vorhandenes Netzwerk importieren
// network = Importer.importNetwork("models/bq.knn");
/// Loss-, Stop- und Optimization-Funktion für das Training festlegen
LossFunction lossFunction = LossFunction.CROSS_ENTROPY_LOSS;
StopFunction stopFunction = new EarlyStopping(0.002, 5);
LearningRateFunction learningRateFunction = new ConstantLearningRate(0.03);
OptimizationFunction optimizationFunction = new GradientDescent(lossFunction, learningRateFunction);
/// Trainer mit Mini-Batching definieren und starten
Trainer trainer = new Trainer(network, 30, true, 10,
lossFunction, stopFunction, optimizationFunction);
trainer.train(train);
/// Evaluierung des trainierten Netzwerks
Scorer scorer = new ClassificationScorer(network);
Score score = scorer.score(test);
score.print();
/// optionaler Export des Netzwerks
// network.export("models/bq_demo.knn");
/// Visualisierung des Netzwerks als Heatmap
HeatmapData heatmapData = new HeatmapData(network);
HeatmapView window = new HeatmapView();
window.addHeatmap(heatmapData, "Manuelle Gewichtsmatrix");
/// Visualisierung des Netzwerks als Sankey-Plot
try {
Platform.startup(() -> {
}); // JavaFx initialisieren
} catch (IllegalStateException ignored) {
} // Ignorieren, falls es schon läuft
SankeyData sankeyData = new SankeyData(network);
new SankeyView(sankeyData, "Manueller Sankey-Plot");
}
}Weitere Code-Beispiele, die während der Entwicklung erstellt wurden und nicht dokumentiert sind, befinden sich ebenfalls in demselben Package de.fhdw.knn.run
Datenaufbereitung
CsvReader
Mit dem CSV-Reader ist es möglich, CSV-Dateien in ein DataSet umzuwandeln. Hier muss einmal der Dateipfad und jeweils der Startindex und die Größe des Inputs sowie Outputs angegeben werden. In der nun vorliegenden Form sind die Daten dann bereit, in Train- und Test-Splits aufgeteilt zu werden. Dabei kann ein Random-Seed und der Anteil der Daten im Test-Set angegeben werden.
DataSet data = CsvReader.readFile("data/banana_quality.csv", 0, 7, 7, 1);
TrainTestSplit trainTest = data.shuffleAndSplit(42, 0.2);
DataSet train = trainTest.train;
DataSet test = trainTest.test;DataSet
Als Rückgabe erhält man ein DataSet, welches man sich wie ein klassisches Tabellenobjekt für maschinelles Lernen vorstellen kann. Es enthält alle Eingabewerte und zugehörigen Ausgabewerte in Form von zweidimensionalen Arrays, wobei jede Zeile einem einzelnen Datenpunkt entspricht. Zusätzlich speichert es Metainformationen wie die Anzahl der Datensätze sowie die Anzahl der Ein- und Ausgabewerte pro Zeile. Darüber hinaus stellt die Klasse Methoden zur Vorverarbeitung bereit, etwa zum Mischen der Daten, Aufteilen in Trainings- und Testdaten oder zur Normalisierung.
Normalizer
Der Normalizer dient dazu, Eingabe- oder Ausgabedaten vor dem Training auf einen einheitlichen Wertebereich zu skalieren. Dadurch werden unterschiedliche Größenordnungen der Features ausgeglichen, was die Stabilität und Konvergenz des Lernalgorithmus verbessert. Der verwendete Normalizer speichert dabei die berechneten Parameter, sodass die Daten bei Bedarf wieder denormalisiert werden können. MinMaxNormalizer orientiert sich dabei an den Min- und Max-Werten der Daten. Bei Bedarf lassen sich weitere Normalizer unter Implementierung des Normalizer-Interfaces implementieren. Weitere Informationen dazu sind in den Java-Docs zu finden.
Normalizer normalizerInputs = new MinMaxNormalizer(-10, 10);
Normalizer normalizerOutputs = new MinMaxNormalizer(-10, 10);
data.normalizeInputs(normalizerInputs);
data.normalizeOutputs(normalizerOutputs);Network
Die Netzstruktur wird in der Network-Klasse aufgebaut. Sie setzt sich aus einem Input-Layer (7 gibt hier die Anzahl der Input-Neuronen im Layer an) mehreren Dense-Layern (denseLayers siehe unten), einem Random-Seed (42) und einem sog. Weight-Initializer zusammen. Da die Erzeugung der Dense-Layer nicht trivial mit der Anzahl der Layer/Neuronen möglich ist, wird hierauf in einem gleich folgenden Abschnitt eingegangen. Jedes erstellte Network ist ein fully-connected Feed-Forward-Network.
Network network = new Network(42, WeightInitializer.GLOROT_UNIFORM, 7, denseLayers);Weight-Initializer
Bei Erstellung eines Networks müssen am Ende die Gewichte der vorher definierten Kanten initialisiert werden. Dafür werden diese Weight-Initializer im Network angegeben. Zu den zur Verfügung stehenden Initializern gehören:
WeightInitializer.ZEROWeightInitializer.HEWeightInitializer.HE_UNIFORMWeightInitializer.GLOROTWeightInitializer.GLOROT_UNIFORM
Input-Layer
Der Input-Layer besteht aus mehreren Input-Neuronen. Er ist so wie ein klassischer Input-Layer zu verstehen. Es gibt keine weiteren Parameter.
Dense-Layer
Der Dense-Layer bildet sowohl die Hidden-Layer als auch den Output-Layer eines neuronalen Netzes ab. Bei der Erstellung werden zwei Aktivierungsfunktionen benötigt. Die Erste ist für jeden Hidden-Layer. Die Zweite ist für den Output-Layer, da es sich als hilfreich erwiesen hat, diese zu unterscheiden. Zusätzlich wird eine beliebige Anzahl von Integer-Werten übergeben, die jeweils die Anzahl der Neuronen pro Schicht festlegen. Jeder dieser Integer-Werte steht für eine eigene Schicht im Netzwerk, wobei der letzte Wert die Größe des Output-Layers bestimmt.
Alternativ kann das Array der Dense-Layer auch manuell mit beliebigen Neuronen und Aktivierungsfunktionen erstellt werden. Die übergebenen Neuronen der DenseLayer werden vom Konstruktor der Netzwerk-Klasse automatisch verbunden (fully-connected, Feed-Forward).
Bei Bedarf können weitere Aktivierungsfunktionen unter Implementierung des ActivationFunction- Interfaces eingebaut werden. Weitere Informationen sind in den Java-Docs zu finden.
DenseLayer[] denseLayers = DenseLayer.createLayers(ActivationFunction.SWISH, ActivationFunction.SIGMOID, 100, 100, 1);Zu den unterstützten Aktivierungsfunktionen gehören:
ActivationFunction.LINEARActivationFunction.RELUActivationFunction.SIGMOIDActivationFunction.SINActivationFunction.SNAKEActivationFunction.SOFTPLUSActivationFunction.SWISHActivationFunction.TANH
Neuronen
Diese Bibliothek liefert verschiedene Neuronen, welche zur Erstellung von KNNs verwendet werden können.
InputNeuron: Neuronen des Input-Layers (ohne weitere Funktion/Parameter)AbstractDenseNeuron: Hat als abstrakte Klasse der Neuronen im Dense-Layer mehrere eingehendeConnections (aus allen Neuronen des vorherigen Layers, jeweils mit Gewicht) und kann eine Ausgabe/Aktivierung berechnen.DenseNeuron: Spezialisierung desAbstractDenseNeuronmit Bias und Aktivierungsfunktion. Verhält sich wie ein klassisches künstliches Neuron.SuperNeuron: Spezialisierung desAbstractDenseNeuron, welches ein ganzes anderes importiertesNetworkbeinhaltet. Somit verhält sich dieses Neuron wie dieses Network und ist nicht von der Optimierungsfunktion des Hauptnetzwerks betroffen.
Bei Bedarf können weitere Neuronen unter Berücksichtigung des AbstractDenseNeurons implementiert werden. Weitere Informationen finden sich in den Java-Docs.
SuperNeuron-Adapter
Zur Erzeugung eines SuperNeurons kann zusätzlich ein Adapter verwendet werden, wenn
- die Anzahl der Input-Neuronen des Netzwerks innerhalb des
SuperNeurons von der Anzahl der Neuronen im Layer vor demSuperNeuronabweicht, - oder nicht nur genau jedes n-te Neuron des vorherigen Layers mit jedem n-ten Input-Neuron des Netzwerks innerhalb des
SuperNeurons verbunden werden soll.
Mithilfe des Adapters wird ein weiterer Input-Layer innerhalb des Netzwerks im SuperNeuron erzeugt. Der Adapter funktioniert so, dass jedes n-te Neuron des dem SuperNeuron vorgelagerten Layers mit dem n-ten Neuron des Adapter-Layers verbunden wird. Die Verbindung eines Neurons in ein SuperNeuron hinein stellt also tatsächlich nur eine Verbindung zu dem (internen) Neuron des SuperNeuron-Adapters dar, welches den gleichen Index hat. Der Adapter passt also das eingebettete Netzwerk im SuperNeuron an das äußere Netzwerk an (Integration).
Der Adapter-Bias gibt den Bias für jedes Neuron des ursprünglichen Input-Layers vom eingebetteten Netzwerk an. Dieser ursprüngliche Input-Layer wird nun zum intern zum ersten Dense-Layer und benötigt also nun einen Bias.
Die Adapter-Weights geben nun die Verbindungen in den ursprünglichen Input-Layer (nun ersten Dense-Layer) vom neuen Input-Layer an. Das zweidimensionale/äußere Array fasst alle Neuronen des ursprünglichen Input-Layers zusammen. Das n-te innere Array im äußeren Array beschreibt alle eingehenden Verbindung aus dem neuen Input-Layer in das n-te Neuron des ursprünglichen Input-Layers. Das m-te Element im n-ten inneren Array gibt die Verbindung vom m-ten Neuron des neuen Input-Layers zum n-ten Neuron des ursprünglichen Input-Layers an.
Das erzeugte Super-Neuron (z.B. mit Adapter) kann anschließend in ein anderes Netzwerk mit Angabe von Layer und Neuron-Index eingefügt werden (insert).
Network includedNetwork = Importer.importNetwork("models/sin_snake.knn");
double[] adapterBias = new double[]{0};
double[][] adapterWeights = new double[][]{
new double[]{1}
};
SuperNeuron superNeuron = new SuperNeuron(includedNetwork, adapterBias, adapterWeights);
superNeuron.insert(network, 0, 0);Hat das äußere Netzwerk vom oberen Beispiel abweichend z.B. 2 Neuronen in dem Layer, das dem Super-Neuron direkt vorgelagert ist, und das eingebettete Netzwerk nur ein Neuron im Input-Layer, muss folgender Adapter verwendet werden:
A1 und A2 sind die neu hinzugefügten Adapter-Neuronen, die nun neu hinzugefügten Input-Layer des Netzwerks innerhalb des Super-Neurons liegen. I1 ist das Neuron des ursprünglichen Input-Layers des eingebetteten Netzwerks, welches nun zum ersten Dense-Layer wird. D1 befindet sich nun im zweiten Dense-Layer (ursprünglich erster Dense-Layer). Hier beschreibt adapterBias[0] den Bias von I1, adapterWeights[0][0] das Gewicht von A1 zu I1 und adapterWeights[0][1] das Gewicht von A2 zu I1. Entsprechend kann der Adapter z.B. wie folgt definiert werden:
double[] adapterBias = new double[]{
7 // Bias von I1
};
double[][] adapterWeights = new double[][]{
new double[]{ // beschreibt alle eingehenden Verbindung zu I1
10, // Gewicht der Verbindung von A1 zu I1
5 // Gewicht der Verbindung von A2 zu I1
}
};IO
Es besteht auch die Möglichkeit, bestehende Networks zu exportieren und diese dann an anderen Stellen wieder zu importieren. Exportiert wird in ein binäres Format, da es viel kompakter ist, als ein menschenlesbares Format.
Network networkToExport = ...
networkToExport.export("models/bq.knn");
Network importedNetwork = Importer.importNetwork("models/bq.knn");WARNING
Das Exportformat ist binär und nicht menschenlesbar. Versionskonflikte zwischen unterschiedlichen Bibliotheksversionen können beim Import zu Fehlern führen.
Trainer
Der Trainer ist die Klasse, welche das Training ausführt. Für das Training müssen mehrere Parameter angegeben werden:
Network, auf dem trainiert wird,- die maximale Anzahl an
Epochenals Integer, - ein Boolean, ob ge
shufflet werden soll, - die
Batch-Size(Mini-Batching mit>1, SGD mit1), - die
Verlust-Funktionzum Ermitteln Qualität des Netzwerks nach jeder Epoche (wird nur zur Ausgabe verwendet, nicht zum Training:nullzum Deaktivieren), - die
Stop-Methodekann das Training vorzeitig beenden, - und die
Optimierungsfunktionermitteln die Anpassungen des Netzwerks (in der RegelGradientDescent, in welchem die tatsächlich zum Training genutzte Verlust-Funktion definiert wird, die von der Verlust-Funktion des Trainers abweichen kann)
LossFunction lossFunction = LossFunction.CROSS_ENTROPY_LOSS;
StopFunction stopFunction = StopFunction.NEVER;
OptimizationFunction optimizationFunction = new GradientDescent(lossFunction, new ConstantLearningRate(0.03));
Trainer trainer = new Trainer(network, 50, true, 1, lossFunction, stopFunction, optimizationFunction);
trainer.train(train);Learning-Rate
Für die Steuerung der Learning-Rate stehen mehrere Strategien zur Verfügung, die das Trainingsverhalten des Modells beeinflussen. Zur Auswahl gehören Constant, Decay, Softstart sowie SoftstartDecay.
Bei Constant bleibt die Lernrate während des gesamten Trainingsprozesses unverändert. Decay reduziert die Lernrate exponentiell über die Trainingszeit hinweg, um gegen Ende stabilere und feinere Anpassungen der Gewichte zu ermöglichen. Softstart beginnt mit einer zunächst kleinen Lernrate, die in den ersten Trainingsepochen um einen konstanten Faktor begrenzt wird, um ein zu starkes initiales Überschwingen zu vermeiden. SoftstartDecay kombiniert beide Ansätze, indem die Lernrate zunächst begrenzt wird (Softstart) und anschließend im weiteren Verlauf wieder kontinuierlich abgesenkt wird (Decay).
Weitere Learningrates können unter Berücksichtigung des LearningRateFunction-Interfaces implementiert werden. Weitere Details sind in den Java-Docs zu finden.
Loss-Function
Bei einem KNN mit dem Gradient-Descent-Optimierungsalgorithmus wird in der Regel eine Verlust-Funktion verwendet, um einerseits die Modellqualität messbar beurteilen zu können und andererseits die Anpassungen/Optimierungen des Netzwerks von dieser Funktion beeinflussen zu lassen.
Die im Folgenden definierte Verlustfunktion kann also einerseits im Trainer zur Ausgabe der Qualität (kleiner Loss) verwendet werden und andererseits in der Optimierungsfunktion GradientDescent, um tatsächlich das Modell mit dieser zu trainieren (beide Angaben können abweichen).
LossFunction lossFunction = LossFunction.CROSS_ENTROPY_LOSS;Diese Bibliothek unterstützt klassische Verlust-Funktionen:
LossFunction.CROSS_ENTROPY_LOSS(entspricht Binary Cross-Entropy Loss)LossFunction.MEAN_SQUARED_ERRORLossFunction.MEAN_ABSOLUTE_ERROR
Bei Bedarf können unter Implementierung des LossFunction-Interfaces weitere Loss-Funktionen hinzugefügt werden. Weitere Informationen sind in den Java-Docs zu finden.
Stop-Criteria
Diese Bibliothek unterstützt außerdem das EarlyStopping, um Overfitting vorzubeugen. Diese Stop-Funktion muss beim Erstellen des Trainers mitgegeben werden. Bislang kann man nur Early-Stopping aktivieren (Erzeugen einer EarlyStopping-Instanz) und deaktivieren (StopFunction.NEVER).
EarlyStopping-Instanz benötigt eine minimale Verbesserung des Loss je Epoche (z.B. 0.01) sowie eine Patience, die angibt wie viele Epochen sich der Loss nicht stärker verbessern darf, vorzeitig abzubrechen (z.B. 10);
StopFunction stopFunctionDisabled = StopFunction.NEVER;
StopFunction stopFunctionEarlyStopping = new EarlyStopping(0.01, 10);Bei Bedarf können weitere Stop-Funktionen unter Berücksichtigung des StopFunction-Interfaces implementiert werden. Weitere Informationen sind unter den Java-Docs zu finden.
Optimization-Function
Unter Optimierungs-Funktionen ist hier die Backpropagation-Funktion zu verstehen. Also mit welchem Vorgehen die kontinuierliche Anpassung der Gewichte passiert. Hier kann aktuell nur der GradientDescent-Algorithmus verwendet werden. Dieser benötigt zur Initialisierung die ausgewählte Verlust-Funktion sowie Learning-Rate.
OptimizationFunction optimizationFunction = new GradientDescent(lossFunction, new ConstantLearningRate(0.03));Bei Bedarf können weitere Optimierungsfunktionen hinzugefügt werden. Dafür muss das OptimizationFunction-Interface implementiert werden. Weitere Implementierungsdetails sind in den Java-Docs zu finden.
Scorer
Das Scorer-Interface kann für einen Datensatz einen Score ermitteln, der ausgegeben werden kann.
Implementiert ist bisher nur der ClassificationScorer, welcher anhand eines DataSets übliche Metriken für Klassifikationsprobleme errechnet. Zu diesen zählen die Confusion Matrix sowie Accuracy, Error, Precision, Recall, F1-Score und werden in der ClassificationScorer.Score-Klasse zusammengefasst. Diese werden dann durch das am Ende des Testings ausgegeben.
Scorer scorer = new ClassificationScorer(network);
Score score = scorer.score(test);
score.print();Visualization
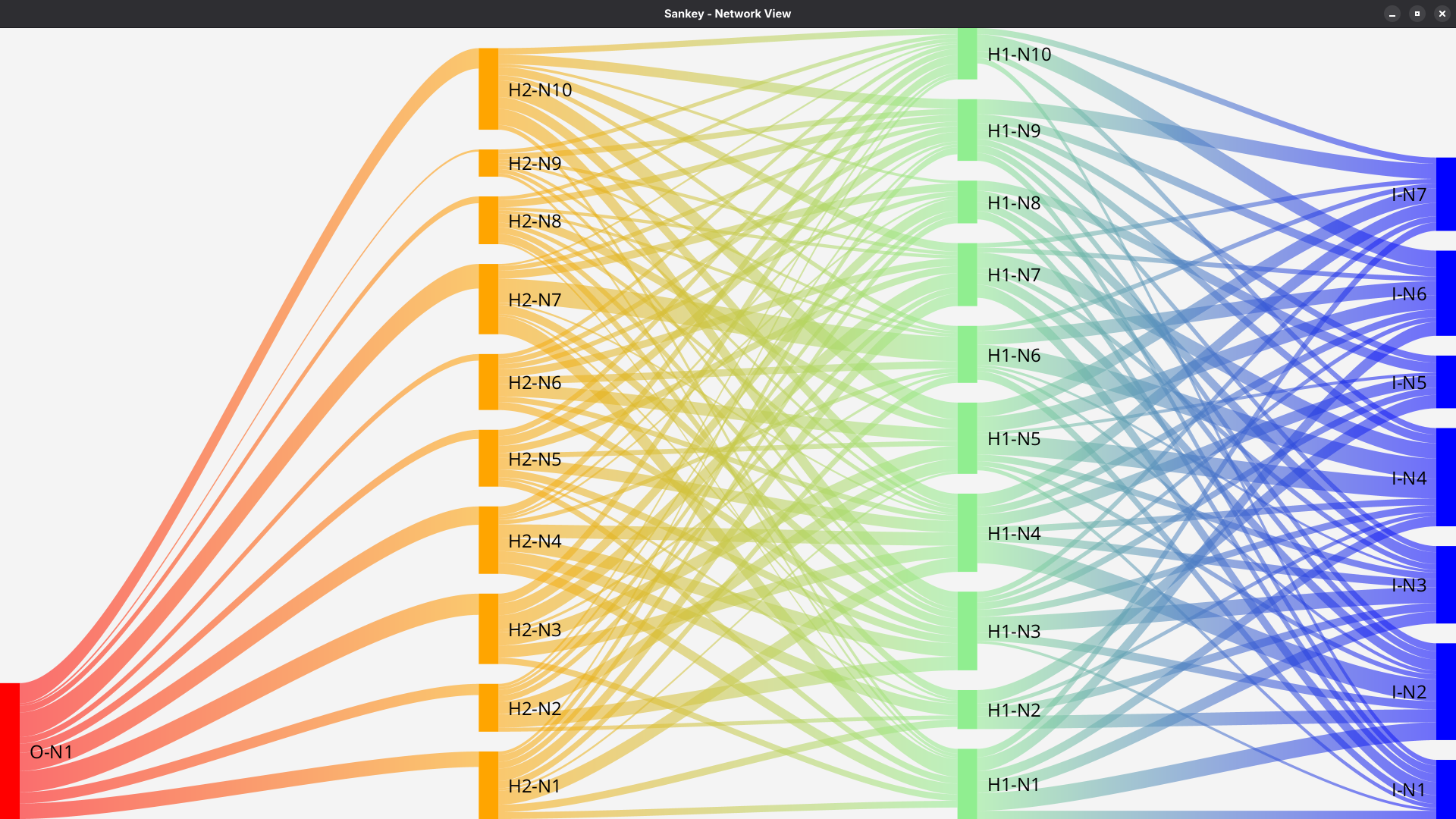
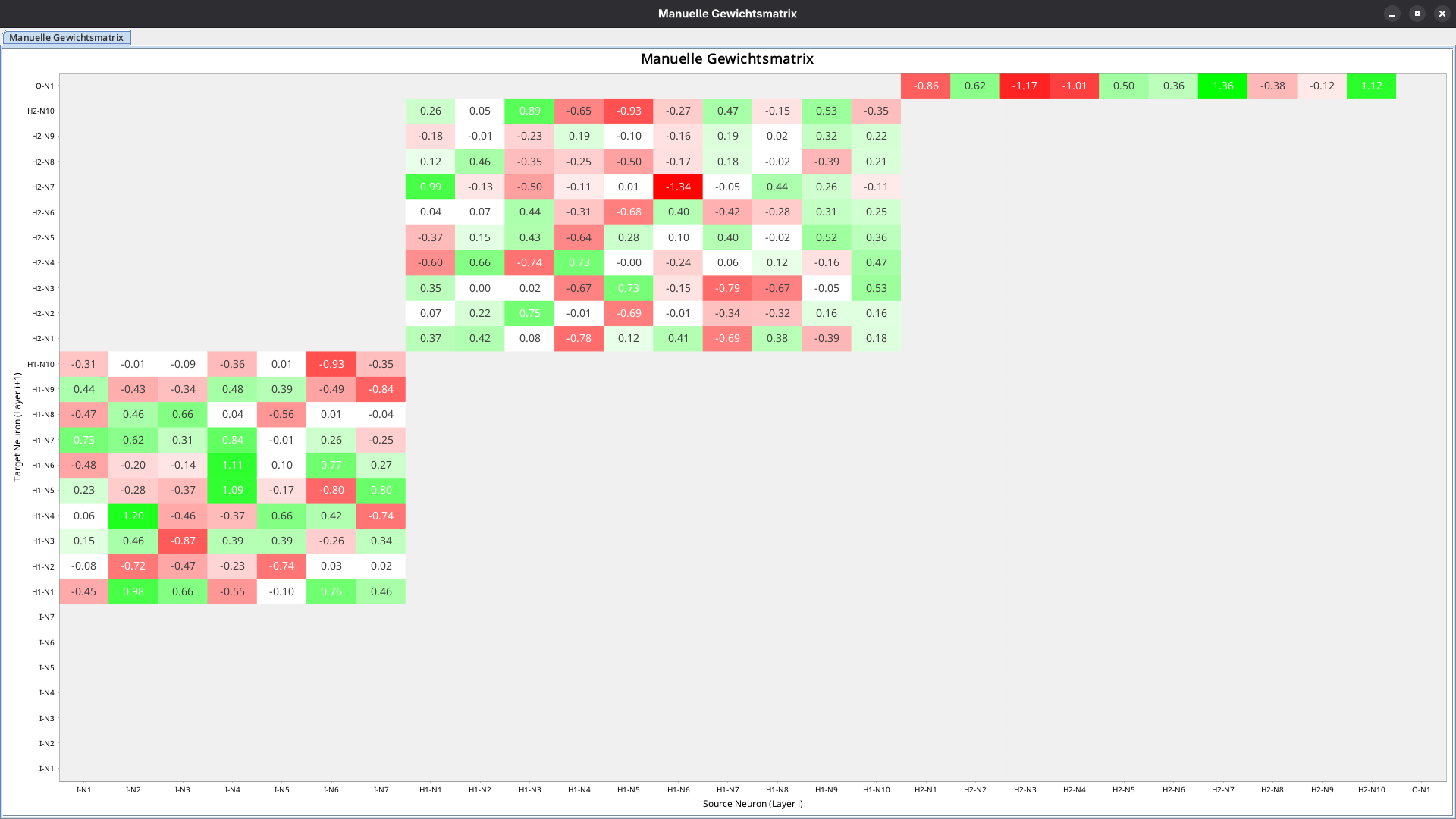
Mithilfe der Netzwerke lassen sich verschiedene Visualisierungen der Ergebnisse darstellen. Dieses Beispiel zeigt die Erstellung einer Heatmap:
HeatmapData heatmapData = new HeatmapData(network);
HeatmapView heatmapView = new HeatmapView();
heatmapView.addHeatmap(heatmapData, "Manuelle Gewichtsmatrix");Networks lassen sich als Heatmap darstellen, in der die x-Achse das Quell-Neuron und die y-Achse das Ziel-Neuron darstellt. Rote Felder stehen standardmäßig für positive Gewichte (verstärkende Verbindungen), grüne Felder für negative Gewichte (hemmende Verbindungen). Je intensiver die Farbe ist, desto größer ist der Einfluss. Weiße Felder liegen unterhalb des konfigurierten Schwellenwertes und gelten als vernachlässigbar. Graue Felder verdeutlichen, dass es keine Verbindungen zwischen den jeweiligen Neuronen gibt.
Der Sankey-Plot stellt die Verbindungen als Linien dar. Je dicker die Linie, desto stärker gewichtet ist die Verbindung.
try {
Platform.startup(() -> {
}); // JavaFx initialisieren
} catch (IllegalStateException ignored) {
} // Ignorieren, falls es schon läuft
new SankeyView(new SankeyData(network), "Manueller Sankey-Plot");