KNN
Dokumentation zur KNN-Bibliothek.
Hier wird die grundlegende Dokumentation anhand von Beispielen erklärt. Detaillierte Informationen zu einzelnen Klassen bzw. Interfaces sind der beiliegenden [Javadoc] zu entnehmen. Ein grober Überblick über die Funktionalität der Bibliothek ist ebenfalls weiter unten zu finden.
Was ist dieses Projekt?
Dieses Projekt ist eine selbst geschriebene Machine-Learning Bibliothek zum Erstellen und Trainieren von KNNs (künstlichen Neuronalen Netzen). Es umfasst das Erstellen von neuronalen Netzen mit und ohne Hidden-Layer, verschiedene Aktivierungs-, Verlust- und Optimierungsfunktionen, einstellbare Trainingsparameter, Visualisierungsmethoden der KNNs und die Möglichkeit, Dateien einzulesen.
Verwendung der Konfiguration
Die Verwendung von TOML-Konfigurationsdateien ist unter configuration.md beschrieben.
Verwendung der Bibliothek
Die Verwendung dieses Projekts als Bibliothek ist unter library.md beschrieben.
Überblick
Funktionalität / Umsetzung
Die Funktionalität der KNN-Bibliothek umfasst die Erstellung und das Training von künstlichen Neuronalen Netzen (KNNs) mit verschiedenen Konfigurationen. Es ermöglicht die Auswahl von Aktivierungsfunktionen, Verlustfunktionen und Optimierungsalgorithmen, um die Leistung der KNNs zu optimieren. Die Bibliothek bietet auch Möglichkeiten zur Visualisierung der KNN-Struktur und der Trainingsfortschritte.
Daten-Verarbeitung
- CSV-Dateien einlesen (inkl. Preprocessing)
- Abstraktion der Daten durch die
DataSet-Klasse - Normalisierung der Daten (z.B.
MinMaxNormalizer) - Train-/Test-Split der Daten
Konfigurierbare Netzwerk-Strukturen
- Feedforward Neural Network
- erweiterbare Aktivierungsfunktionen: ReLU, Swish, Sigmoid, Snake, Softplus, Tanh, Linear, Sinus
- erweiterbare Gewichtsinitialisierungen: Glorot/Xavier (Normal, Uniform), He (Normal, Uniform), Zero
- Flexible Anzahl Neuronen im Input Layer
- Flexible Anzahl Dense Layer mit konfigurierbarer Anzahl Neuronen
- Verzicht auf Hidden Layer möglich
- Hilfsmethoden zum einfachen Erstellen mehrerer Dense-Layer (üblicher Strukturen)
- verschiedene Neuronen-Arten: Input Neuronen, Dense Neuronen, Super Neuronen
- Integration komplexer Strukturen in einzelne Neuronen möglich (Super Neuronen)
- Super Neuronen können als Container für Subnetze dienen (mit Adapter für die Integration in das Hauptnetz)
- Unterstützung von Verbindungs-Gewichten und -Guards sowie Bias und Aktivierungsfunktionen
Konfigurierbare Trainings-Parameter
- erweiterbare Verlustfunktionen: Mean Squared Error (MSE), Mean Absolute Error (MAE), Binary Cross-Entropy Loss (BCE)
- erweiterbare Learning Rates: konstant, exponentiell abnehmend (Decay), gedämpfter Start (Softstart), SoftstartDecay (kombiniert)
- erweiterbare Optimierungs-Algorithmen: Gradient Descent
- Backpropagation auf Basis analytisch berechneter Gradienten
- erweiterbare Stop-Funktionen: Early Stopping
- basierend auf Verlustfunktion
- konfigurierbare Anzahl Epochen und Batch-Größe (z.B. Mini-Batching oder SGD)
- parallelisiertes Batch-Training (Multi-Threading) für große Batch-Größen
- dynamischer Export während des Trainings (z.B. alle n Epochen)
- Visualisierung des Netzes während des Trainings
- zufälliges Mischen der Trainings-Daten (randomisierter Shuffle mit Seed für Reproduzierbarkeit)
Modell-Export/Import
- Export von trainierten Modellen in Dateien
- kompaktes/effizientes Format (binär)
- Import von Modellen aus Dateien
- Export/Import inklusive Subnetzen (z.B. Super Neuronen)
- Export und Import erzeugen 100% identisches Modell
- Export von trainierten Modellen in Dateien
Evaluierung
- Evaluierung der Modell-Performance auf Testdaten
- erweiterbare Scorer: Classification Scorer (für Klassifikationsprobleme)
- Berechnung der True/False Positives/Negatives
- Berechnung von Metriken wie Accuracy, Error, Precision, Recall, F1-Score
- Evaluierung der Modell-Performance auf Testdaten
Visualisierung
- Visualisierung der KNN-Struktur (Verbindungen/Gewichte zwischen Neuronen)
- auch live während des Trainings möglich (z.B. alle n Epochen)
- Heatmap der Gewichte
- Sankey-Plot der Verbindungsstärken
- Visualisierung der KNN-Struktur (Verbindungen/Gewichte zwischen Neuronen)
Bibliothek oder TOML-Config
- programmatische Erstellung von KNNs über die Java-API
- erweiterter Funktionsumfang (z.B. durch Implementierung von Interfaces)
- volle Kontrolle inklusive Pre-/Post-Processing
- deklarative Erstellung häufiger Anwendungsfälle über TOML-Konfigurationsdateien
- Daten-Verarbeitung
- Netzwerk-Struktur
- Trainings-Parameter
- Export/Import
- Evaluierung
- Visualisierung
- programmatische Erstellung von KNNs über die Java-API
Flexibilität / Interoperabilität
Anwendung auf verschiedene Datensätze und Problemstellungen
- z.B. Regression, Klassifikation, Monoalphabetische Substitution
- keine Einschränkung auf bestimmte Problemstellungen
- flexible Konfiguration der Netzwerk-Struktur und Trainings-Parameter ermöglicht Anpassung an verschiedene Anwendungsfälle
Erweiterbarkeit durch Implementierung definierter Interfaces
- Normalizer
- Aktivierungsfunktionen
- Gewichtsinitialisierungen
- Optimierungsalgorithmen
- Verlustfunktionen
- Stop-Funktionen
- Learning-Rate-Funktionen
- Scorer
- individuelle Dense Neuronen (nur bei Erweiterung des Optimierungsalgorithmus)
Effizienz / Performance
- Multithreading für Batch-Training
- Parallelisierung der Backpropagation
- Parallelisierung der Netzwerk-Anpassung
- effiziente Wiederverwendung allokierter Arrays
- Ziel: Zero-Allocation (Heap) während des Trainings
- Arrays für Anpassungen/Adjustments nur zu Beginn allokieren und wiederverwenden
- Performance-Verbesserung um ca. 30%
- stabile Speicherauslastung (Entlastung des Garbage Collectors)
- Neuron-Ausgabe in wiederverwendbarem Buffer
- Optimierungsalgorithmus während Trainings-Epoche immutable und thread-safe
- Multithreading trotz wiederverwendeter Buffer
- Parallelisierung des Feedforward bei Vorhersage für große DataSets
- Netzwerk ist während Feedforward immutable und thread-safe
- Vergleichbare Performance wie scikit-learn je nach Trainings-Parametern
- schneller für kleine Batch-Größen (z.B. SGD)
- Batch-Größe 1:
23.78s(KNN-Bibliothek) vs.175.51s(scikit-learn) - Batch-Größe 4:
26.25s(KNN-Bibliothek) vs.45.47s(scikit-learn) - Batch-Größe 8:
19.67s(KNN-Bibliothek) vs.23.98s(scikit-learn) - Batch-Größe 16:
14.16s(KNN-Bibliothek) vs.13.19s(scikit-learn) - Batch-Größe 32:
12.93s(KNN-Bibliothek) vs.7.54s(scikit-learn) - Batch-Größe 64:
12.45s(KNN-Bibliothek) vs.5.23s(scikit-learn)
- Batch-Größe 1:
- Beispiel für die Messung: Konfiguration
conf/bq_perf.toml- CPU: AMD Ryzen 5 3600 (6 Kerne, 4.2 GHz)
- scikit-learn siehe [assets/bq_perf.py]
- schneller für kleine Batch-Größen (z.B. SGD)
Dokumentation
Eine ausführliche Dokumentation zu diesem Projekt ist in drei Teilen verfügbar:
- TOML-Konfigurationsdateien: configuration.md
- Java-Bibliothek (grundlegend): library.md
- Javadoc (detailliert): [javadoc]
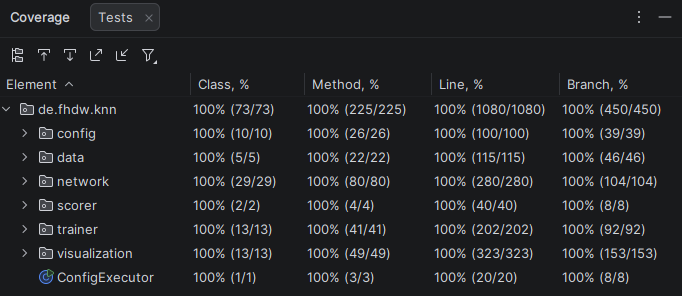
Testvolumen
Zur Sicherstellung der Qualität und Stabilität des Codes wurden umfangreiche Tests zum Erreichen einer Branch (und Line) Coverage von 100% implementiert (ausgenommen davon sind lediglich die experimentellen und isolierten Klassen im Package de.fhdw.knn.run). Um darüber hinaus die Testabdeckung weiter zu erhöhen, wurden nach Erreichen der Branch Coverage von 100% zusätzlich Tests automatisiert generiert (z.B. mithilfe von GitHub Copilot). Diese generierten Testfälle wurden manuell überprüft und anschließend mit der Annotation @Generated gekennzeichnet, um sie von manuell erstellten Tests zu unterscheiden und das verwendete Tool anzugeben.
- manuell erstellte Tests zur Abdeckung aller wichtigen Anwendungsfälle und Randfälle
- 100% Branch Coverage (experimentelles Package
de.fhdw.knn.runausgenommen) - 100% Line Coverage (experimentelles Package
de.fhdw.knn.runausgenommen)
- 100% Branch Coverage (experimentelles Package
- manuell überprüfte, automatisiert generierte Tests (mit
@Generated-Annotation) zur Erhöhung der Testabdeckung - Durchführung von Regressionstests nach Code-Änderungen
- 265 Testfälle insgesamt
- Coverage Report siehe [test_coverage]